Article 15 sur un total de 48 pour la série :
Les génomes comparés aux textes anciens (2)
Dans le dernier billet, nous avons parlé des caractéristiques que l’on attendrait en comparant les génomes d’espèces similaires, si ces espèces descendaient effectivement d’une population ancestrale commune. En utilisant notre analogie du « livre » pour les génomes, nous avons montré que la première chose que nous chercherions serait une structure commune aux deux génomes que l’on suppose descendre d’un génome ancestral commun : les « chapitres », les « paragraphes », etc…, sont-ils dans le même ordre ? Utilisent-ils les mêmes « phrases » ? etc… En d’autres termes, les génomes des espèces actuelles ressemblent-ils à des copies légèrement modifiées les uns des autres ?
La réponse donnée à cette question par la génomique comparative est positive. Ce que l’on voit quand on compare les génomes des espèces dont nous soupçonnons la parenté c’est qu’ils ressemblent effectivement à des copies. Dans certains cas, les correspondances entre les deux génomes excèdent les 95% au niveau de l’ADN pour l’ensemble des deux génomes. Ils n’ont pas seulement les mêmes gènes, mais ils sont dans le même ordre sur les chromosomes, chaque chromosome correspondant à un autre chromosome dans l’autre espèce. Imaginez que vous trouvez un livre identique à 95% à un autre manuscrit, contenant des chapitres, des paragraphes et des phrases dans le même ordre, avec seulement quelques différences entre eux – c’est ce type d’impression que l’on a lorsqu’on compare des génomes de certaines espèces.
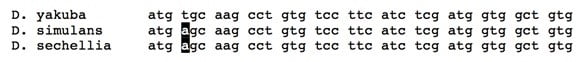
Les mouches à fruits (qu’on appelle drosophiles) sont des espèces qui ont été analysées en détail. Les scientifiques ont aujourd’hui déterminé les séquences d’ADN complètes de douze espèces de drosophiles et les ont comparées. Certaines espèces ont des génomes quasiment identiques, exactement comme on l’aurait prédit si elles avaient formé auparavant une seule espèce avec un génome commun. S’il n’est pas possible de montrer une longue séquence d’ADN ici, nous pouvons examiner un petit fragment d’une « phrase » (c’est-à-dire d’un gène) de trois espèces de mouches à fruits (Drosophila yakuba, Drosophila simulans, et Drosophila sechellia) – toutes connues pour être des espèces distinctes de mouches :
La première impression que l’on a lorsqu’on regarde les séquences c’est qu’elles sont presque identiques. Ce n’est pas inhabituel pour ces trois espèces – en effet, ce patron s’applique à chaque gène qu’elles ont (et elles ont toutes les mêmes gènes). La deuxième chose que l’on remarque, cependant, c’est qu’il y a de rares différences – dans ce tout petit extrait, deux espèces (D. simulans et D. sechellia) ont un « a » en quatrième position de ce gène, alors que D. yakuba a un « t ».
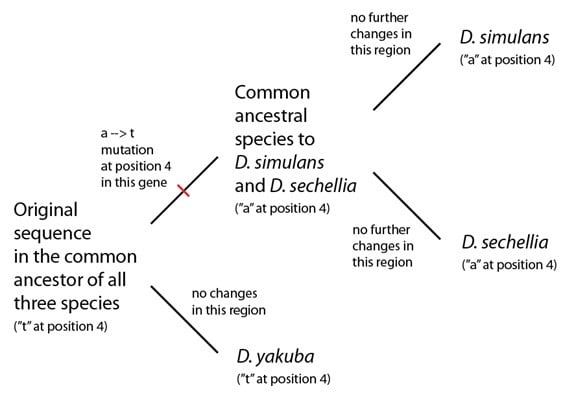
Rappelez-vous l’analogie que nous avons utilisée la dernière fois, celle des éditions d’un livre et les fautes de frappe qu’elles partagent. Les séquences de ces trois espèces sont comme les éditions hypothétiques que nous avons utilisées dans notre analogie, et nous pouvons expliquer le patron que nous observons à peu près de la même façon :
(Des lecteurs consciencieux noteront aussi que l’autre possibilité est que le “a” en quatrième position soit le texte d’origine, que le “t” soit une faute de frappe, et que la mutation (t à a) soit arrivée une fois dans le lignage qui a conduit à D. yakuba. Si vous réfléchissez à cette option, bien joué. Ce qui permet de décider quel est le texte d’origine, c’est de regarder autant de copies que possibles – et dans ce cas, lorsque nous regardons un grand nombre d’autres espèces drosophiles, nous voyons un « t » en quatrième position dans la plupart des espèces, et un « a » seulement chez D. simulans et D. sechellia. Cela signifie que le choix le plus économique est que le « t » est l’original, et que le « a » est une mutation.)
Ce n’est qu’un petit exemple, mais il illustre ce que les scientifiques observent quand ils comparent les génomes d’espèces dont ils soupçonnent la parenté en se basant sur d’autres critères (comme la morphologie). Ce qu’ils voient correspond précisément à ce à quoi l’on s’attendrait si des événements de spéciation avaient effectivement eu lieu pour produire les espèces en question : des génomes quasiment identiques, avec de petits changements partagés entre certaines espèces.
Une identité plus forte au niveau de l’ADN que nécessaire pour conserver la fonction du gène.
Une autre observation qui soutient l’hypothèse que ces séquences sont les copies d’une séquence ancestrale est que le niveau d’identité (de séquence correspondante) entre elles est plus haut que ce qui est requis, même lorsque la fonction du gène est considérée. Retournons au fragment de gène que nous examinions. Cette séquence, en tant que point de départ d’un gène, code une protéine qui a la même fonction dans les trois espèces. (Si vous avez besoin de vous rafraîchir la mémoire sur la façon dont les gènes sont fabriqués en monomères d’ADN qui sont ensuite traduits en une séquence d’acides aminés, vous pouvez vous référer à ces deux billets précédents.) Dans ces espèces, la séquence de cette protéine pour les huit premiers acides aminés est la suivante:
Comme vous pouvez le voir, le second acide aminé est différent dans les deux séquences, mais les autres sont identiques. Ce qu’il est important de comprendre c’est qu’il y a de nombreuses façons d’écrire cette « phrase » et d’arriver à la même signification (séquence d’acides aminés). Cela est possible parce que pour la plupart des acides aminés, il existe plusieurs combinaisons de trois nucléotides (qu’on appelle des codons) qui produisent le même acide aminé quand il est traduit. Par exemple, la séquence de D. yakuba pourrait aussi être écrite comme suit (c’est une option parmi beaucoup d’autres) :
Cette séquence est assez différente de ce que nous voyons dans les deux autres espèces :
Dans ce cas, seuls 14 des 27 nucléotides correspondent – une identité d’environ 52% seulement. Ce que nous observons cependant, c’est que 26 des 27 nucléotides correspondent (plus de 96% d’identité). En d’autres termes, il serait possible pour ces deux gènes d’être plus ou moins identiques à l’échelle de l’ADN et d’avoir quand même les mêmes séquences d’acides aminés que nous observons dans les deux espèces. Pourtant, ce que nous voyons lorsque nous comparons les deux gènes, c’est qu’au niveau de l’ADN, ils correspondent bien plus que ce qui est nécessaire pour avoir les mêmes séquences d’acides aminés. Une explication simple est que les deux séquences correspondent parce qu’elles sont des copies de la même séquence d’origine.
L’identité dépasse ce qui est nécessaire pour la fonction à l’échelle des acides aminés.
Une seconde observation qui soutient l’hypothèse selon laquelle les séquences de gène de D. yakuba, de D. simulans et de D. sechellia sont en fait des copies vient de l’examen d’autres espèces de mouches qui sont moins proches de ces trois espèces. Toutes les espèces de drosophiles examinées jusqu’à aujourd’hui ont ce gène, mais dans des parents plus éloignés cette séquence peut être quelque peu différente. Par exemple, ce gène de D. mojavensis a la séquence ADN suivante :
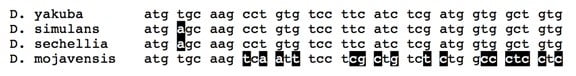
Une fois encore, une partie de la séquence demeure identique dans les quatre espèces (ce qui soutient l’hypothèse que cette séquence est aussi une copie, mais avec plus de changements), mais nous voyons maintenant de plus grandes différences. Malgré ces différences, la version du gène de D. mojavensis est parfaitement fonctionnelle et accomplit exactement le même travail que le gène des trois autres espèces plus proches.
Ces observations indiquent qu’il n’y a aucun besoin biologique pour que des gènes soient presque identiques au niveau des acides aminés, ou même au niveau de l’ADN chez ces différentes espèces. De nombreuses séquences d’acides aminés, et même de nombreuses séquences d’ADN sont également capables d’accomplir la même fonction. Pourtant ce que nous voyons de manière récurrente (sur les génomes tout entiers !) sont des gènes presque identiques, avec quelques différences (souvent partagées) – exactement ce que l’on attendrait d’événements de spéciation.
Qu’en est-il du “dessein commun” ?
Lorsque je présente ces données, on me demande souvent si le « dessein commun » ne pourrait pas être une autre explication possible. En d’autres termes, ces types de patrons pourraient-ils être expliqués en maintenant qu’ils sont des espèces créées séparément, sans ancêtre commun, mais qu’elles ont été créées pour avoir des gènes identiques ou similaires parce que ces gènes ont besoin de fonctions identiques ou similaires ?
Nous avons déjà vu les problèmes que pose cette ligne d’argumentation – les gènes (et le génome tout entier) d’espèces similaires correspondent bien plus qu’il n’est nécessaire – et que les différences que nous voyons dans des espèces à parenté proche sont arrangées sur le patron que l’on prédirait si des événements de spéciation les avaient produits.
Rien que des mouches
Bien sûr, la possibilité que de nombreuses espèces de mouches à fruits se soient déployées au cours du temps par de multiples événements de spéciation n’empêche pas la plupart des chrétiens de dormir. Comme nous l’avons déjà mentionné, même la plupart des créationnistes de la jeune terre acceptent de tels événements de spéciation. Ce qui est plus contentieux, bien entendu, c’est la question de savoir si le patron de l’ancêtre commun s’étend à notre propre espèce. Dans le prochain billet de notre série, nous examinerons cette question en comparant le génome humain aux génomes de ceux qui pourraient être nos parents vivants les plus proches – les grands singes.
48 Articles pour la série :
- 01-L’évolution expliquée : Introduction
- 02-L’Evolution : Une théorie testée, pas une simple hypothèse !
- 03-Biogéographie
- 04-Une introduction à la variation, à la sélection naturelle et artificielle
- 05-Les chiens domestiques
- 06-Comment ça marche, la sélection naturelle ?
- 07-La sélection naturelle et le lignage humain.
- 08-Les bases de la variation héréditaire, première partie
- 09-Les bases de la variation héréditaire, deuxième partie.
- 10-De la variation à la spéciation (1)
- 11-De la variation à la spéciation (2)
- 12-De la variation à la spéciation 3
- 13-De la variation à la spéciation (4)
- 14-Les génomes sont comme des anciens textes (1)
- 15-Les génomes comparés aux textes anciens (2)
- 16-Les génomes comparés aux textes anciens (3): les origines de l’homme
- 17-Le génome comparé à un texte ancien (4)
- 18-Le génome comparé à un texte ancien (5): rattacher le tout ensemble.
- 19-Les arbres généalogiques des espèces, des gènes, et tri incomplet des lignées
- 20-Tri de lignage incomplet et taille d’une population ancestrale
- 21-Une introduction à l’homoplasie et à la convergence évolutive
- 22-Evolution convergente et homologie profonde.
- 23-Coévolution et la course à l’armement prédateur / proie
- 24-Le parasitisme, le mutualisme et la co-spéciation
- 25-Comprendre l’endosymbiose
- 26-La diversification cambrienne et la mise en place des plans d’organisation animaux. Première partie.
- 27-La diversification cambrienne et la mise en place des plans d’organisation animaux. 2e partie.
- 28-La mise en place des plans d’organisation des corps vertébrés, première partie.
- 29-La mise en place des plans d’organisation des corps vertébrés, deuxième partie.
- 30-La mise en place des plans d’organisation des vertébrés : Troisième partie.
- 31-La mise en place des plans d’organisation des vertébrés, quatrième partie.
- 32-Des reptiles aux mammifères.
- La révolution placentaire : deuxième partie.
- Du primate à l’humain, première partie.
- Du primate à l’humain, deuxième partie
- Du primate à l’humain (3)
- La paléontologie hominienne : une petite esquisse des preuves actuelles
- Devenir humain (1) : Eve mitochondriale et Adam Y-chromosomique
- Analogie entre évolution biologique et évolution du langage
- Devenir humain (3) : paléogénomiques et la toile emmêlée de la spéciation humaine
- 41-L’évolution, Partie 1: frontières scientifiques, abiogenèse et apologétique chrétienne
- 42-Aux frontières de l’évolution, Partie 2: l’abiogenèse et la question du naturalisme
- 43-Aux frontières de l’évolution, Partie 3 : l’hypothèse du monde à ARN
- 44-Aux frontières de l’évolution, partie 4 : Contingence versus convergence
- 45-Aux frontières de l’évolution, partie 5 : Contigence versus convergence dans l’expérience LTEE
- 46- L’évolution et le chrétien, première partie: Est-ce que l’évolution est un mécanisme sans but ?
- 47- L’évolution et le chrétien, deuxième partie: Une créature merveilleuse
- 48- L’évolution et le chrétien, partie 3 : Dire la vérité dans l’amour